Approfondir notre compréhension du cerveau humain au cours du développement
Le Projet de génomique fonctionnelle du cerveau (GPBF) est une initiative multidisciplinaire de l'Institut du cerveau de Paris qui vise à construire une ressource intégrée reliant l'expression spatiale des gènes, la distribution des protéines et la fonction des gènes dans le cerveau en développement.
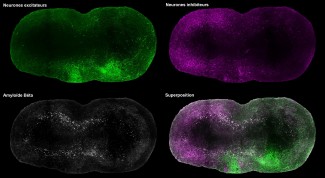
Le projet s'articule autour de trois objectifs complémentaires. Le premier objectif consiste à développer un nouveau workflow combinant l'hybridation in situ en fluorescence de l'ARN 3D (3D RNA FISH) avec la transcriptomique spatiale (Visium HD, Visium V2, GeoMx) et la protéomique spatiale sur les mêmes échantillons de tissus. Appliquée au tissu foetal humain et au tissu cérébral de souris à des stades clés du développement, cette approche générera un atlas multimodal spatialement résolu de l'expression des gènes au cours du développement du cerveau. Le second objectif consiste à établir une plate-forme de dépistage fonctionnelle basée sur le knockdown génique médié par CRISPRi chez les organoïdes corticaux dérivés de iPSC. À l'aide de systèmes dCas9 inductibles et constitutifs, l'écran évaluera systématiquement l'impact de la régulation négative des gènes associés à la maladie sur la neurogenèse, établissant un lien direct entre la fonction des gènes et les phénotypes neurodéveloppementaux. Le troisième objectif vise à développer l'infrastructure de calcul nécessaire pour intégrer ces ensembles de données, y compris les pipelines pour l'alignement d'images 3D à 3D et 3D à 2D, l'analyse de la transcriptomique spatiale à résolution monocellulaire et les bases de données de métadonnées assurant une traçabilité complète de l'échantillon aux données.
Ensemble, ces trois objectifs produiront le premier atlas reliant les profils d'expression des gènes spatiaux aux rôles fonctionnels des gènes dans le cerveau en développement. Le projet tire parti des capacités technologiques uniques de l'institut et favorise la collaboration interdisciplinaire entre biologistes expérimentaux, ingénieurs et spécialistes des données. Tous les outils, les pipelines et les ensembles de données seront mis à la disposition du milieu de la recherche selon les principes de la science ouverte.
Ambition
Pour comprendre comment le cerveau se développe et comment ce processus se déroule mal dans les maladies neurologiques et psychiatriques, il faut plus que répertorier quels gènes sont exprimés où. Elle exige une vision intégrée — une vision qui capte l'expression des gènes dans son contexte tissulaire tridimensionnel natif, la relie à la distribution des protéines et relie les profils spatiaux à la fonction des gènes. C'est précisément l'ambition du projet de génomique fonctionnelle du cerveau. En combinant, pour la première fois sur les mêmes échantillons, l'ARN 3D FISH avec la transcriptomique spatiale et la protéomique spatiale, et en couplant cet atlas multimodal avec le dépistage fonctionnel systématique chez les organoïdes corticaux humains, BFGP produira une ressource qui comblera l'écart entre l'expression spatiale des gènes et la fonction biologique au cours du développement du cerveau. Aucun atlas existant n'offre ce niveau d'intégration. Les outils de calcul et les pipelines d'analyse développés dans le cadre du projet rendront cette ressource entièrement accessible et reproductible, établissant ainsi une plate-forme ouverte pour la communauté des neurosciences. En fin de compte, en révélant où, quand et dans quels types de cellules agissent les gènes associés aux maladies — et ce qui se passe quand ils sont perturbés —, BFGP jettera les bases de la compréhension des mécanismes cellulaires par lesquels le risque génétique se traduit en maladie neurologique, et de l'identification des populations cellulaires et des fenêtres de développement les plus pertinentes pour les stratégies thérapeutiques futures.
AIM-1: Un nouveau paradigme pour le profilage spatial multimodal des tissus intacts.
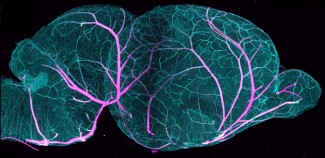
Les technologies de transcriptomique spatiale ont transformé notre compréhension de la distribution de l'ARN à l'intérieur des tissus, offrant des perspectives inédites sur l'organisation cellulaire et l'architecture tissulaire. Cependant, les approches actuelles demeurent largement confinées à de minces sections bidimensionnelles, ce qui limite notre capacité de saisir la structure tridimensionnelle complexe d'organes comme le cerveau. Notre projet s'attaque à cette limite fondamentale. Le workflow développé dans AIM-1 est, à notre connaissance, le premier protocole permettant la détection de cibles multiples d'ARN en trois dimensions par l'ARN 3D FISH (six gènes répartis sur deux rondes d'hybridation), suivi de la transcriptomique spatiale (Visium HD, Visium V2 ou GeoMx) et de la protéomique spatiale (jusqu'à 20 anticorps) — tous réalisés de façon séquentielle sur le même échantillon. Cette stratégie multimodale, qui consiste à prélever un même échantillon, est particulièrement cruciale pour les spécimens rares et irremplaçables, comme les tissus cérébraux fœtaux humains ou les échantillons de tumeurs provenant de patients, où chaque section doit fournir un maximum d'information. L'article sur la méthode actuellement en préparation — couvrant à la fois le protocole expérimental et la filière d'analyse associée — devrait avoir un impact significatif dans de multiples domaines, y compris les neurosciences du développement, la neuro-oncologie et toute discipline nécessitant un profilage moléculaire spatialement résolu de tissus complexes. Au-delà des neurosciences, le workflow est en principe applicable à tout type d'organe ou de tissu, et sa diffusion ouverte permettra son adoption par d'autres laboratoires dans le monde entier.
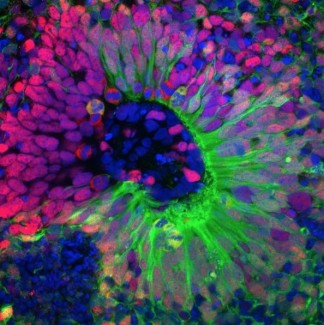
AIM-2: Une plateforme de dépistage fonctionnelle accessible pour la biologie du neurodéveloppement.
Ces dernières années ont vu des progrès significatifs dans le dépistage fonctionnel à grande échelle dans des modèles organoïdes tridimensionnels, principalement par des approches regroupées dans lesquelles des milliers de perturbations génétiques sont introduites simultanément et lues par séquençage d'une seule cellule (p. ex., CROP-seq, Perturb-seq chez les organoïdes). Bien que les écrans puissants et groupés soient limités dans les dimensions phénotypiques qu'ils peuvent capter: les lectures sont généralement limitées aux changements de transcriptomie, et les phénotypes spatiaux ou morphologiques — qui sont essentiels à la compréhension du développement du cerveau — sont largement inaccessibles. Notre projet adopte une approche fondamentalement différente en développant une plate-forme de dépistage arrangée CRISPRi chez les organoïdes corticaux dérivés d'iPSC, dans laquelle chaque gène renversé est réalisé et phénotypé individuellement. Ce format arrangé permet l'évaluation de phénotypes riches et multidimensionnels incluant la morphologie, la composition cellulaire, l'organisation spatiale et l'activité neuronale — dont aucun ne peut être capturé facilement dans un contexte de regroupement. À notre connaissance, il s'agit du premier effort visant à établir un criblage systématique arrangé à l'échelle chez les organoïdes corticaux. Le développement à la fois d'un système lentiviral inductible et d'un système constitutif tout-en-un fournit des outils d'administration flexibles compatibles avec les modèles expérimentaux mis en place. L'important travail de dépannage et d'optimisation effectué durant cette période — y compris la résolution des problèmes de fuites Cre et de détection GCaMP — représente des connaissances pratiques qui profiteront à tout groupe tentant des approches similaires. Ces outils et protocoles fourniront à la communauté un cadre accessible pour la génomique fonctionnelle arrangée dans les systèmes organoïdes, comblant une lacune critique entre les approches de dépistage groupées et les études mécanistes détaillées. À plus long terme, la capacité de phénotyper les chutes de gènes individuelles dans un modèle tridimensionnel pertinent pour l'humain ouvre la porte à l'identification non seulement des gènes liés à la maladie, mais aussi des phénotypes cellulaires et structurels spécifiques par lesquels ils agissent — information essentielle pour prioriser les cibles thérapeutiques.
AIM-3: Infrastructure de calcul ouverte pour l'intégration multimodale des données.
L'intégration d'ensembles de données spatiales hétérogènes — imagerie volumétrique 3D, transcriptomique spatiale 2D, protéomique spatiale — pose des défis de calcul auxquels aucune suite logicielle disponible sur le marché ne répond entièrement. Les pipelines développés dans AIM-3 pour l'enregistrement d'images 3D-à-3D, l'alignement 3D-à-2D et l'analyse spatiale monocellulaire basée sur la segmentation nucléaire représentent des contributions inédites aux communautés de l'informatique des bioimages et de l'analyse spatiale omique. Ces outils sont élaborés dans l'optique d'une diffusion libre, ce qui assure leur reproductibilité et leur large accessibilité. Les bases de métadonnées conçues pour assurer la traçabilité des échantillons aux données répondent également à un besoin croissant sur le terrain d'une gestion rigoureuse des données dans des flux de travail expérimentaux complexes en plusieurs étapes — une condition préalable à la reproductibilité de la science et au partage futur des données en vertu des principes FAIR. Ces contributions vont au-delà de nos questions biologiques spécifiques et seront pertinentes pour tout groupe travaillant avec des données spatiales multimodales, en neurosciences ou dans d'autres disciplines biomédicales.
Pris ensemble, les trois buts du GPBF apportent un cadre technologique intégré — des tissus aux données en passant par la biologie — qui n'existait pas auparavant. En rendant tous les protocoles, outils et ensembles de données ouvertement disponibles, le projet est conçu pour servir de ressource communautaire plutôt que de plate-forme fermée. La combinaison des données de l'atlas spatial avec les résultats du dépistage fonctionnel a le potentiel de remodeler la façon dont la communauté des neurosciences priorise les gènes candidats des maladies, en fournissant non seulement des cartes d'expression, mais aussi des preuves directes de la fonction des gènes dans un modèle de développement pertinent pour l'humain. Cette approche est transférable à d'autres systèmes organiques et contextes de maladie, et nous prévoyons que les contributions méthodologiques du GPBF auront un impact durable sur la façon dont les expériences multimodales de biologie spatiale sont conçues, exécutées et analysées.